
Back Basispaar Afrikaans زوج قاعدي Arabic Базова двойка Bulgarian Bazni par BS Parell de bases Catalan Párování bází Czech Basepar Danish Basenpaar German Base pair English Baza paro Esperanto

|
|
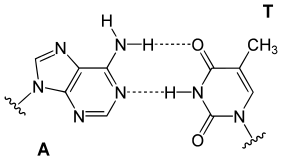
Em genética e biologia molecular um par de bases consiste em dois nucleotídeos opostos e complementares nas cadeias de ADN e ARN que estão conectadas por ligações de hidrogênio (frequentemente chamadas pb ou do inglês base pair, bp).
Na canônica paridade de bases Watson-Crick, adenina (A) forma um par de base com timina (T), como a guanina (G) faz par com a citosina (C) no DNA. No ARN, a timina é substituída pelo uracilo (U), conectando-se este com a adenosina. A paridade de base não nos moldes Watson-Crick com alternados padrões de ligações de hidrogênio também ocorre, especialmente no RNA; tais padrões comuns são os pares de bases Hoogsteen.
Paridade é também o mecanismo pelo qual códons sobre moléculas de RNA mensageiro são reconhecidas por anticódons sobre RNA transferência durante a translação de proteína. Algumas enzimas de ligação DNA ou RNA podem reconhecer padrões de paridade de bases específicas que identificam regiões de genes de regulação particular.
O tamanho de um gene individual ou um genoma inteiro de um organismo é frequentemente medido nos pares de bases. O DNA é normalmente de cadeia dupla. Desde que, o número total de pares de bases é igual ao número de nucleotídeos numa das cadeias (com a exceção de regiões de cadeia única não codificada de telômeros). O genoma humano haploide (23 cromossomas) é estimado como tendo aproximadamente o comprimento de 3 bilhões de pares de bases e contendo de 20 a 25 mil genes distintos.[1]
Uma quilobase (em algumas obras kilobase) é uma unidade de medida em biologia molecular significando 1 000 pares de bases de DNA ou RNA.